在当前许多各种不同的生物学研究中,用于产生和理解全局基因表达分析数据的常见假设能够导致关于基因活性和细胞行为方面严重缺陷性的结论。相关研究结果刊登在Cell期刊上。
怀海德研究所研究员Richard Young说,“表达分析是当代生物学最经常用到的方法之一。因此,我们担心存在缺陷的假设可能影响对很多生物学研究的理解。”
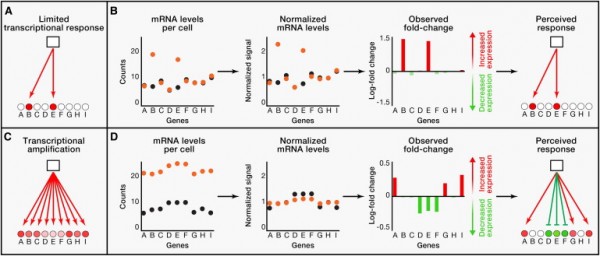
今天对基因表达数据的大多数理解都依赖于一种假设:用来分析的所有细胞拥有类似的mRNA总量,其中mRNA大约占细胞RNA中的10%,作为蛋白合成的蓝图发挥作用。然而,一些细胞,包括恶性癌细胞,要比其他细胞产生几倍多的mRNA。传统的全局基因表达分析通常忽略这些差别。
Young实验室研究员和论文共同通讯作者Tony Lee说,“我们着重研究了基因表达分析的这种常见性的假设,它潜在影响了很多研究人员。我们提供一种具体的问题例子和一种研究人员能够执行的解决方法。”
Young实验室的成员们最近在研究表达高水平c-Myc的癌细胞的基因表达时揭示出这种缺陷。已知c-My是一种基因调节物,在恶性癌细胞中高度表达。当比较表达高水平c-Myc的细胞和表达低水平c-Myc的细胞时,他们吃惊地发现不同的基因表达分析方法能够产生显著性的不同结果。进一步的研究揭示出在含有高水平c-Myc的和低水平c-Myc的细胞中存在显著性的不同,不过这些不同利用常见使用的实验方法和分析方法来掩盖掉。
论文共同作者Jakob Lovén说,“我们从不同的基因表达分析方法中观察到的不同结果是令人震惊的,而且导致我们在几种平台上重新研究了这整个过程。我们然后意识到细胞含有类似mRNA水平的常见假设存在严重缺陷,能够导致严重性的误解,特别是对拥有非常不同RNA含量的癌细胞而言,尤其如此。”
除了描绘出这种问题之外,研究人员也描述了一种补救方法。通过利用被称作RNA spike-in的人工合成mRNA作为标准对照,他们能够比较实验数据并且能够消除关于细胞RNA总量方面的假设。他们将这种补救方法应用到他们研究的所有三种基因表达分析平台。
尽管研究人员相信使用RNA spike-in应当成为全局基因表达分析的新标准,但是理解很多之前的研究时产生的问题可能持续存在。
以上中文部分来自生物谷:http://www.bioon.com/biology/Class18/531901.shtml
更多关于基因表达的信息,请继续阅读PLoB上更多文章:https://www.plob.org/tag/%E5%9F%BA%E5%9B%A0%E8%A1%A8%E8%BE%BE
更多原文请原文:
Revisiting Global Gene Expression Analysis
Jakob Lovén, David A. Orlando, Alla A. Sigova, Charles Y. Lin, Peter B. Rahl, Christopher B. Burge, David L. Levens, Tong Ihn Lee, Richard A. Young
Gene expression analysis is a widely used and powerful method for investigating the transcriptional behavior of biological systems, for classifying cell states in disease, and for many other purposes. Recent studies indicate that common assumptions currently embedded in experimental and analytical practices can lead to misinterpretation of global gene expression data. We discuss these assumptions and describe solutions that should minimize erroneous interpretation of gene expression data from multiple analysis platforms.
全文链接:http://www.sciencedirect.com/science/article/pii/S0092867412012263