A. 主成分分析
主成分分析(principal components analysis, PCA)是一种分析、简化数据集的技术。它把原始数据变换到一个新的坐标系统中,使得任何数据投影的第一大方差在第一个坐标(称为第一主成分)上,第二大方差在第二个坐标(第二主成分)上,依次类推。主成分分析经常用减少数据集的维数,同时保持数据集的对方差贡献最大的特征。这是通过保留低阶主成分,忽略高阶主成分做到的。这样低阶成分往往能够保留住数据的最重要方面。但是在处理观测数目小于变量数目时无法发挥作用,例如基因数据。
R语言中进行主成分分析可以采用基本的princomp函数,将结果输入到summary和plot函数中可分别得到分析结果和碎石图。但psych扩展包更具灵活性。
一、选择主成分个数
选择主成分个数通常有如下几种评判标准:
- 根据经验与理论进行选择
- 根据累积方差的门槛值,例如选择使累积方差达到80%的主成分个数。
- 根据相关系数矩阵的特征值,选择特征值大于1的主成分。
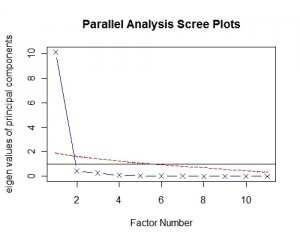
另一种较为先进的方法是平行分析(parallel analysis)。该方法首先生成若干组与原始数据结构相同的随机矩阵,求出其特征值并进行平均,然后和真实数据的特征值进行比对,根据交叉点的位置来选择主成分个数。我们选择USJudgeRatings数据集举例,首先加载psych包,然后使用fa.parallel函数绘制下图,从图中可见第一主成分位于红线上方,第二主成分位于红线下方,因此主成分数目选择1。
[code lang="R"]
fa.parallel(USJudgeRatings[,-1], fa="pc", n.iter=100, show.legend=FALSE)
[/code]
二、提取主成分
[code lang="R"]
pc=principal(USJudgeRatings[,-1],nfactors=1)
[/code]
PC1 h2 u2 1 0.92 0.84 0.1565 2 0.91 0.83 0.1663 3 0.97 0.94 0.0613 4 0.96 0.93 0.0720 5 0.96 0.92 0.0763 6 0.98 0.97 0.0299 7 0.98 0.95 0.0469 8 1.00 0.99 0.0091 9 0.99 0.98 0.0196 10 0.89 0.80 0.2013 11 0.99 0.97 0.0275
从上面的结果观察到,PC1即主成分负荷,是观测变量与主成分之间的相关系数,h2是变量能被主成分解释的比例,u2则是不能解释的比例。
三、旋转主成分
旋转是将主成分负荷进行变换,以方便解释。可分为正交旋转和斜交旋转。正交旋转的流行方法是方差最大化,需要在principal中增加rotate='varimax'参数
四、计算主成分得分
主成分得分是各变量的线性组合,需在principal中增加score参数,结果将存放在scores中。但注意如果输入数据不是原始数据时,则无法计算主成分得分。
B. 探索性因子分析
探索性因子分析(Exploratory Factor Analysis,EFA)是一项用来找出多元观测变量的本质结构、并进行处理降维的技术。 因而,EFA能够将将具有错综复杂关系的变量综合为少数几个核心因子。
EFA和PCA的区别在于:PCA中的主成分是原始观测变量的线性组合,组合的选择是在各主成分无关条件下使其方差最大化。而EFA中的因子是影响原始观测变量的潜在变量,变量中不能被因子所解释的部分称为误差,因子和误差均不能直接观察到。进行EFA需要大量的样本,一般经验认为如何估计因子的数目为N,则需要有5N到10N的样本数目。
虽然EFA和PCA有本质上的区别,但在分析流程上有相似之处。下面我们用ability.cov这个心理测量数据举例,其变量是对人的六种能力,例如阅读和拼写进行了测验,其数据是一个协方差矩阵而非原始数据。R语言中stats包中的factanal函数可以完成这项工作,但这里我们使用更为灵活的psych包。
一、选择因子个数
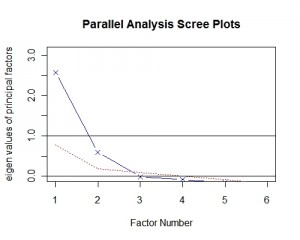
一般选择因子个数可以根据相关系数矩阵的特征值,特征值大于0则可选择做为因子。我们使用平行分析法(parallel analysis)。该方法首先生成若干组与原始数据结构相同的随机矩阵,求出其特征值并进行平均,然后和真实数据的特征值进行比对,根据交叉点的位置来选择因子个数。根据下图我们可以观察到特征值与红线的关系,有两个因子都位于红线上方,显然应该选择两个因子。
library(psych)
covariances <- ability.cov$cov
correlations <- cov2cor(covariances)
fa.parallel(correlations, n.obs=112, fa="fa", n.iter=100,show.legend=FALSE)
[/code]
其中:
library(psych)下载:http://inside-r.org/packages/cran/psych
ability.cov:http://inside-r.org/r-doc/datasets/ability.cov
cov2cor:http://inside-r.org/r-doc/stats/cov2cor
二、提取因子
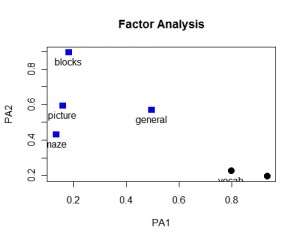
psych包中是使用fa函数来提取因子,将nfactors参数设定因子数为2,rotate参数设定了因子旋转,最后的fm表示分析方法,由于极大似然方法有时不能收敛,所以此处设为迭代主轴方法。从下面的结果中可以观察到两个因子解释了60%的总方差。Reading和vocabulary这两个变量于第一项因子有关,而picture、blocks和maze变量与第二项因子有关,general变量于两个因子都有关系。
fa = fa(correlations,nfactors=2,rotate="varimax",fm="pa" )
[/code]
PA1 PA2 h2 u2
general 0.49 0.57 0.57 0.432
picture 0.16 0.59 0.38 0.623
blocks 0.18 0.89 0.83 0.166
maze 0.13 0.43 0.20 0.798
reading 0.93 0.20 0.91 0.089
vocab 0.80 0.23 0.69 0.313
PA1 PA2
SS loadings 1.83 1.75
Proportion Var 0.30 0.29
Cumulative Var 0.30 0.60还可以用图形来表示因子和变量之间的关系
[code lang="R"]
factor.plot(fa,labels=rownames(fa$loadings))
[/code]
三、因子得分
如果输入的是原始数据,则可以在fa函数中设置score=T参数来获得因子得分。因子和原始变量之间的权重关系则存在结果的weights元素中。
C. 多维标度分析
多维标度分析(MDS)是一种将多维空间的研究对象简化到低维空间进行定位、分析和归类,同时又保留对象间原始关系的数据分析方法。
设想一下如果我们在欧氏空间中已知一些点的座标,由此可以求出欧氏距离。那么反过来,已知距离应该也能得到这些点之间的关系。这种距离可以是古典的欧氏距离,也可以是广义上的“距离”。MDS就是在尽量保持这种高维度“距离”的同时,将数据在低维度上展现出来。从这种意义上来讲,主成分分析也是多维标度分析的一个特例。
一、距离的度量
多元分析中常用有以下几种距离,即绝对值距离、欧氏距离(euclidean)、马氏距离(manhattan)、 两项距离(binary)、明氏距离(minkowski)。在R中通常使用disk函数得到样本之间的距离。MDS就是对距离矩阵进行分析,以展现并解释数据的内在结构。
在经典MDS中,距离是数值数据表示,将其看作是欧氏距离。在R中stats包的cmdscale函数实现了经典MDS。它是根据各点的欧氏距离,在低维空间中寻找各点座标,而尽量保持距离不变。
非度量MDS方法中,“距离"不再看作数值数据,而只是顺序数据。例如在心理学实验中,受试者只能回答非常同意、同意、不同意、非常不同意这几种答案。在这种情况下,经典MDS不再有效。Kruskal在1964年提出了一种算法来解决这个问题。在R中MASS包的isoMDS函数可以实现这种算法,另一种流行的算法是由sammon函数实现的。
二、经典MDS
下面我们以HSAUR2包中的watervoles数据来举例。该数据是一个相似矩阵,表示了不同地区水田鼠的相似程度。首先加载数据然后用cmdscales进行分析。
library(ggplot2)
data(watervoles, package = "HSAUR2")
data(watervoles)
voles.mds=cmdscale(watervoles,k=13,eig=T)
[/code]
下面计算前两个特征值在所有特征值中的比例,这是为了检测能否用两个维度的距离来表示高维空间中距离,如果达到了0.8左右则表示是合适的。
[code lang="R"]
sum(abs(voles.mds$eig[1:2]))/sum(abs(voles.mds$eig))
sum((voles.mds$eig[1:2])^2)/sum((voles.mds$eig)^2)
[/code]
然后从结果中提取前两个维度的座标,用ggplot包进行绘图。
[code lang="R"]
x = voles.mds$points[,1]
y = voles.mds$points[,2]
p=ggplot(data.frame(x,y),aes(x,y,label = colnames(watervoles)))
p+geom_point(shape=16,size=3,colour='red')+
geom_text(hjust=-0.1,vjust=0.5,alpha=0.5)
[/code]
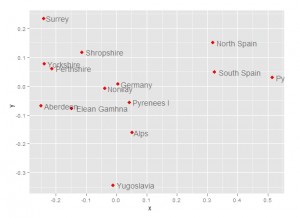
三、非度量MDS
第二例子中的数据是关于新泽西州议员投票行为的相似矩阵,这里我们用MASS包中的isoMDS函数进行分析
[code lang="R"]
library("MASS")
data(voting, package = "HSAUR2")
voting_mds = isoMDS(voting)
x = voting_mds$points[,1]
y = voting_mds$points[,2]
g=ggplot(data.frame(x,y),aes(x,y,label = colnames(voting)))
g+geom_point(shape=16,size=3,colour='red')+
geom_text(hjust=-0.1,vjust=0.5,alpha=0.5)
[/code]
D. 判别分析
判别分析(discriminant analysis)是一种分类技术。它通过一个已知类别的“训练样本”来建立判别准则,并通过预测变量来为未知类别的数据进行分类。
判别分析的方法大体上有三类,即Fisher判别、Bayes判别和距离判别。Fisher判别思想是投影降维,使多维问题简化为一维问题来处理。选择一个适当的投影轴,使所有的样品点都投影到这个轴上得到一个投影值。对这个投影轴的方向的要求是:使每一组内的投影值所形成的组内离差尽可能小,而不同组间的投影值所形成的类间离差尽可能大。Bayes判别思想是根据先验概率求出后验概率,并依据后验概率分布作出统计推断。距离判别思想是根据已知分类的数据计算各类别的重心,对未知分类的数据,计算它与各类重心的距离,与某个重心距离最近则归于该类。
1.线性判别
当不同类样本的协方差矩阵相同时,我们可以在R中使用MASS包的lda函数实现线性判别。lda函数以Bayes判别思想为基础。当分类只有两种且总体服从多元正态分布条件下,Bayes判别与Fisher判别、距离判别是等价的。本例使用iris数据集来对花的品种进行分类。首先载入MASS包,建立判别模型,其中的prior参数表示先验概率。然后利用table函数建立混淆矩阵,比对真实类别和预测类别。
library(MASS)
model1=lda(Species~.,data=iris,prior=c(1,1,1)/3)
table(Species,predict(model1)$class)
[/code]
Species setosa versicolor virginica setosa 50 0 0 versicolor 0 48 2 virginica 0 1 49
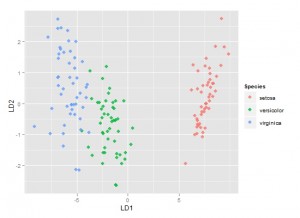
从以上结果可观察到判断错误的样本只有三个。在判别函数建立后,还可以类似主成分分析那样对判别得分进行绘图
[code lang="R"]
ld=predict(model1)$x
p=ggplot(cbind(iris,as.data.frame(ld))
,aes(x=LD1,y=LD2))
p+geom_point(aes(colour=Species),alpha=0.8,size=3)
[/code]
2.二次判别
当不同类样本的协方差矩阵不同时,则应该使用二次判别。
model2=qda(Species~.,data=iris,cv=T)
[/code]
这里将CV参数设置为T,是使用留一交叉检验(leave-one-out cross-validation),并自动生成预测值。这种条件下生成的混淆矩阵较为可靠。此外还可以使用predict(model)$posterior提取后验概率。
在使用lda和qda函数时注意:其假设是总体服从多元正态分布,若不满足的话则谨慎使用。
参考资料:
Modern Applied Statistics With S
Data_Analysis_and_Graphics_Using_R__An_Example_Based_Approach
E. 聚类分析
聚类分析(Cluster Analysis)是根据“物以类聚”的道理,对样品或指标进行分类的一种多元统计分析方法,它是在没有先验知识的情况下,对样本按各自的特性来进行合理的分类。
聚类分析被应用于很多方面,在商业上,聚类分析被用来发现不同的客户群,并且通过购买模式刻画不同的客户群的特征;在生物上,聚类分析被用来动植物分类和对基因进行分类,获取对种群固有结构的认识;在因特网应用上,聚类分析被用来在网上进行文档归类来修复信息。
聚类分析有两种主要计算方法,分别是凝聚层次聚类(Agglomerative hierarchical method)和K均值聚类(K-Means)。
一、层次聚类
层次聚类又称为系统聚类,首先要定义样本之间的距离关系,距离较近的归为一类,较远的则属于不同的类。可用于定义“距离”的统计量包括了欧氏距离(euclidean)、马氏距离(manhattan)、 两项距离(binary)、明氏距离(minkowski)。还包括相关系数和夹角余弦。
层次聚类首先将每个样本单独作为一类,然后将不同类之间距离最近的进行合并,合并后重新计算类间距离。这个过程一直持续到将所有样本归为一类为止。在计算类间距离时则有六种不同的方法,分别是最短距离法、最长距离法、类平均法、重心法、中间距离法、离差平方和法。
下面我们用iris数据集来进行聚类分析,在R语言中所用到的函数为hclust。首先提取iris数据中的4个数值变量,然后计算其欧氏距离矩阵。然后将矩阵绘制热图,从图中可以看到颜色越深表示样本间距离越近,大致上可以区分出三到四个区块,其样本之间比较接近。
data=iris[,-5]
dist.e=dist(data,method='euclidean')
heatmap(as.matrix(dist.e),labRow = F, labCol = F)
[/code]
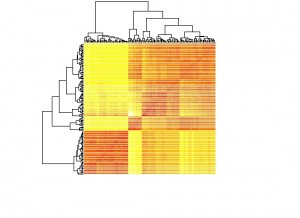
然后使用hclust函数建立聚类模型,结果存在model1变量中,其中ward参数是将类间距离计算方法设置为离差平方和法。使用plot(model1)可以绘制出聚类树图。如果我们希望将类别设为3类,可以使用cutree函数提取每个样本所属的类别。
[code lang="R"]
model1=hclust(dist.e,method='ward')
result=cutree(model1,k=3)
[/code]
为了显示聚类的效果,我们可以结合多维标度和聚类的结果。先将数据用MDS进行降维,然后以不同的的形状表示原本的分类,用不同的颜色来表示聚类的结果。可以看到setose品种聚类很成功,但有一些virginica品种的花被错误和virginica品种聚类到一起。
[code lang="R"]
mds=cmdscale(dist.e,k=2,eig=T)
x = mds$points[,1]
y = mds$points[,2]
library(ggplot2)
p=ggplot(data.frame(x,y),aes(x,y))
p+geom_point(size=3,alpha=0.8,
aes(colour=factor(result),
shape=iris$Species))
[/code]
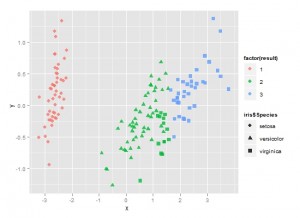
二、K均值聚类
K均值聚类又称为动态聚类,它的计算方法较为简单,也不需要输入距离矩阵。首先要指定聚类的分类个数N,随机取N个样本作为初始类的中心,计算各样本与类中心的距离并进行归类,所有样本划分完成后重新计算类中心,重复这个过程直到类中心不再变化。
在R中使用kmeans函数进行K均值聚类,centers参数用来设置分类个数,nstart参数用来设置取随机初始中心的次数,其默认值为1,但取较多的次数可以改善聚类效果。model2$cluster可以用来提取每个样本所属的类别。
[code lang="R"]
model2=kmeans(data,centers=3,nstart=10)
[/code]
使用K均值聚类时需要注意,只有在类的平均值被定义的情况下才能使用,还要求事先给出分类个数。一种方法是先用层次聚类以决定个数,再用K均值聚类加以改进。或者以轮廓系数来判断分类个数。改善聚类的方法还包括对原始数据进行变换,如对数据进行降维后再实施聚类。
cluster扩展包中也有许多函数可用于聚类分析,如agnes函数可用于凝聚层次聚类,diana可用于划分层次聚类,pam可用于K均值聚类,fanny用于模糊聚类。
来源:http://xccds1977.blogspot.com