写在前面
以下内容均来自我在菲沙基因(Frasergen)暑期生信培训班上记录的课堂笔记
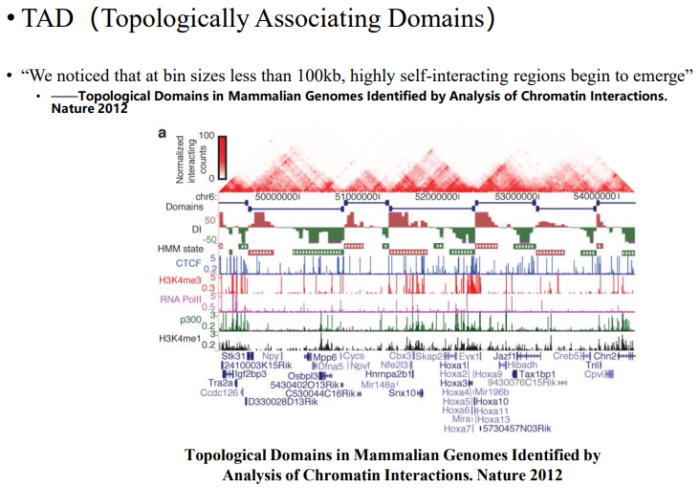
1.TAD
2.TAD分析流程
- 2.1 Cworld-dekker软件的安装
git clone https://github.com/blajoie/cworld-dekker.git #Change directory to the `cworld-dekker` and install the `Perl` module: perl Build.PL ./Build ./Build install --install_base /your/custom/dir (ensure /your/custom/dir is added to your PERL5LIB path) #e.g. ./Build install --install_base ~/perl5 # then in .bashrc export PERL5LIB=${PERL5LIB}:/home/<yourusername>/perl5/lib/perl52.2 分析所用数据
互作图谱分染色体matrix数据(单染色的矩阵),如何获得请看:三维基因组技术(三):Hi-C 数据比对及HiC-Pro的使用
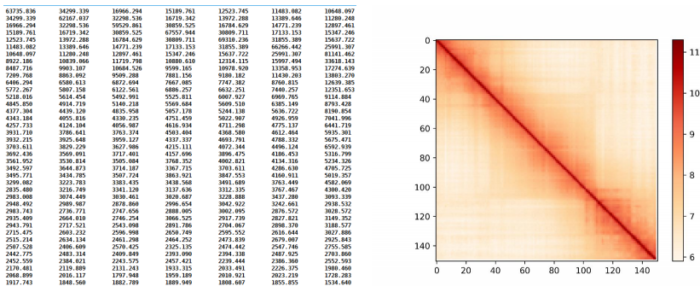
matrix数据
- 2.3 为矩阵添加header
header文件需要自己准备,操作采用cworld的addMatrixHeaders为矩阵文件添加header
perl -I /software/cworld-dekker/ \ /software/cworld-dekker/scripts/perl/addMatrixHeaders.pl \ -i data/example.matrix \ --xhf data/headerxchr2 \ --yhf data/headerychr2
-I:添加cworld的库,连接到cworld软件所在目录即可
-i:matrix 文件
--xhf:横坐标表头
--yhf:纵坐标表头
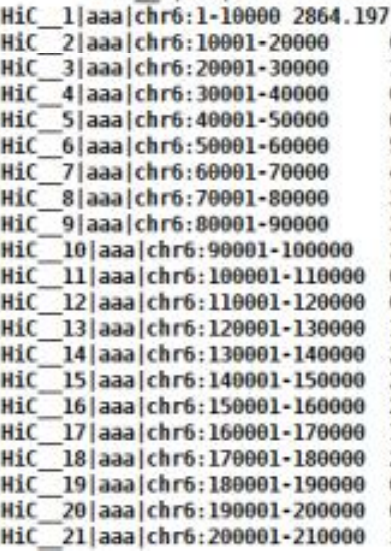
自制Header文件,横纵坐标可以相同,和上一次的不同就是,分辨率更小了(10kb),形如:
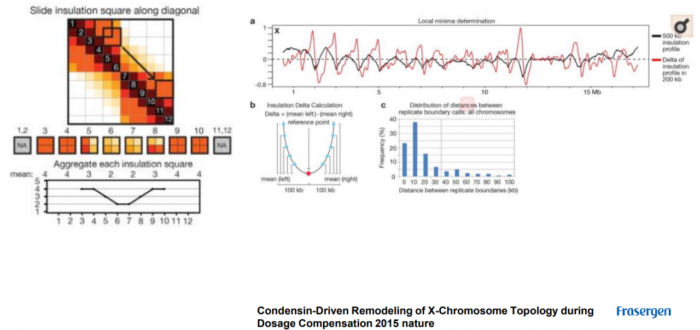
- 2.4 TAD边界鉴定
#export PATH=/local_data1/train/software/R/R-3.5.0/bin/:$PATH #export PATH=/local_data1/train/software/bedtools/bedtools2-2.28.0/bin/:$PATH perl -I /software/cworld-dekker/ \ /software/cworld-dekker/scripts/perl/matrix2insulation.pl \ --is 100000 --ids 40000 \ -i example.addedHeaders.matrix.gz
-I:cworld-dekker的库
--is:方框的大小,最好是矩阵分辨率的整倍数(如50kb),好计算
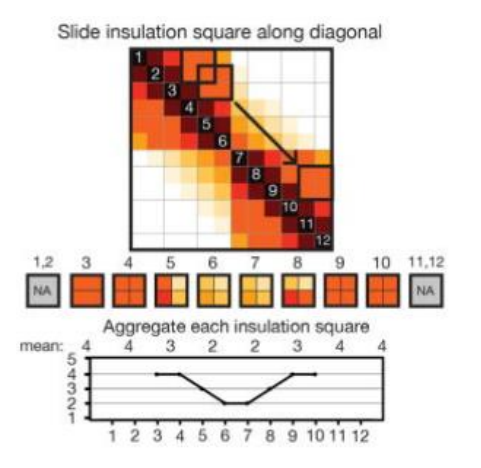
--ids:window size of insulationd delta,矩阵分辨率的整倍数(如20kb),好计算
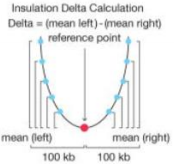
-i:input matrix file,必须是单染色的矩阵,防止划框移动到其他染色体上
- 结果文件以boundaries结尾


- 2.5 结果整理
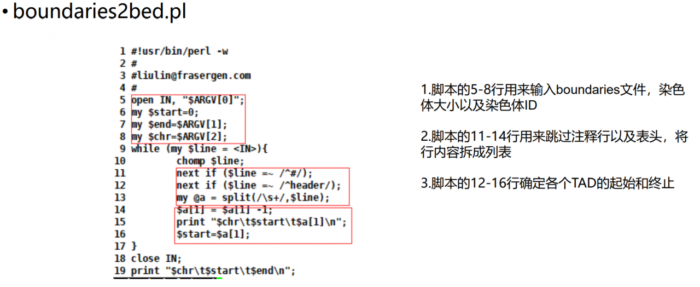
perl boundaries2bed.pl \ example.addedHeaders--is100000--nt0--ids40000--ss0--immean.insulation.boundaries \ 17718942 chr6 > example.tad.bed
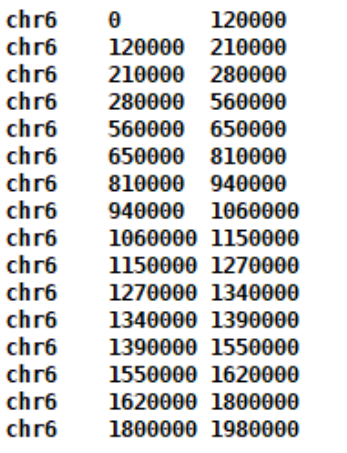
TAD的范围