多序列比对在分子生物学中是一个基本方法,用来发现特征序列,进行蛋白分类,证明序列间的同源性,帮助预测新序列二级结构与三级结构,确定PCR引物,以及在分子进化分析方面均有很大帮助,Clustal W(Dos版本)很适合这些方面的要求,Clustal X是window版本。
用Clustal比对后的序列,有时候我们需要转为图片放在文章作详细方析,但大部分人的方法都是直接截图,这样的后果就是图片一点都不美观。如果你是想要发表文章或其它比较重要的用途,图片的质量还是需要高一点的。
今天LIUCHENG.NAME教大家如何把ClustalX的结果转为漂亮的图片的方法,你可以根据需要设置每一行显示的字母数,是黑白的还是彩色的,够酷吧。先来看个效果图吧。
这里需要用到两个软件,一个是Clustal X,这个就不用说了。这时相信你已经有了clusalX序列比对后的结果,有两个文件,一个是.aln文件,存放多序列比对的结果。一个是.dnd文件,根据需要,可以转为系统发育树图,这个就不在今天的教程内了,有需要以后可以讲,-:)。
现在重点讲另一个软件,DnaMan。DNAMAN美国Lynnon Biosoft公司开发的高度集成化的分子生物学应用软件,几乎可完成所有日常核酸和蛋白质序列分析工作,包换多重序列对齐、PCR引物设计、限制性酶切分析、蛋白质分析、质粒绘图等。可往这里下载:
http://www.pharmnet.com.cn/conf/rjsj /action.cgi?f=page_1_&t=page_1_&id=98227
1,打开DnaMan,依次打开“文件/打开指定的/多重比对”,载入Clustal X比对后的.aln文件
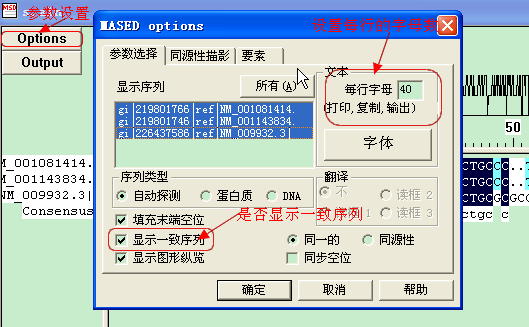
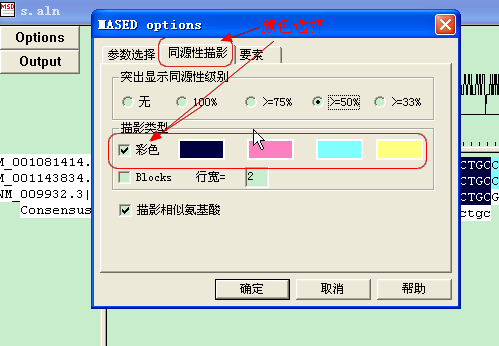
2,点击options,参数设置,在这里,你可以设置每行显示的序列,是否显示一致序列,彩色或黑白等。
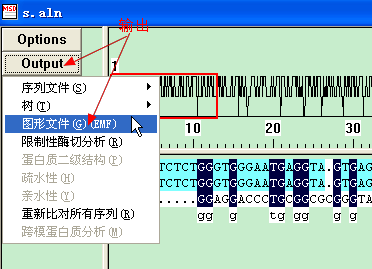
3,点击Output,输出为图形文件,这样子就大功告成了,如果还不满意,可以在参数设置进行微调,直到你满意为止。这里需要注意,每次输出图片都要命名为不同的文件名,好象不会覆盖,这个比较奇怪。深色部分表示完全匹配的碱基,浅色为部分匹配。
From:http://blog.sina.com.cn/u/1944457820





1F
很好的一个技巧,赞一个
2F
好,解决了我的问题,谢谢!