实体关系图
实体
| 名称 | 定义 | ||
| Pathway | specifies graph information stored in the KEGG pathway map | 代谢通路图 | path:ko00010 |
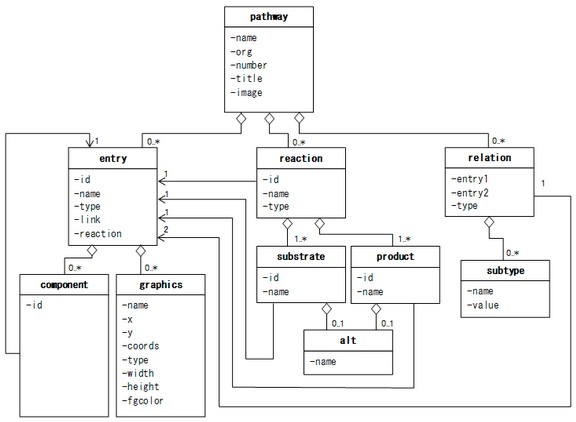
| Entry | The entry element contains information about a node of the pathway. | 节点信息 | |
| Component | a subelement of the entry element, and is used when the entry element is a complex node; namely, when the type attribute value of the entry element is “group”. | 组件,一个复杂的节点,比如节点为Group类型时,包含的节点,可以存放到组件中 | |
| Graphics | a subelement of the entry element, specifying drawing information about the graphics object. | 节点在图位信息 | |
| Relation | relationship between two proteins (gene products) or two KOs (ortholog groups) or protein and compound, which is indicated by an arrow or a line connecting two nodes in the KEGG pathways. | 节点之间的关系 | |
| Subtype | more detailed information about the nature of the interaction or the relation. | 节点之间关系的更详细信息 | |
| Reaction | chemical reaction between a substrate and a product indicated by an arrow connecting two circles in the KEGG pathways. | 在KEGG通路中,用两个圆圈加箭头表示底物与产物之间的化学反应。 | rn:(accession)rn:R02749 |
| Substrate | the substrate node of this reaction. | 反应的底物 | cpd:(accession) gl:(accession) |
| Product | the product node of this reaction. | 产物 | cpd:(accession) gl:(accession) |
| Alt | the alternative name of its parent element. | 别名 | cpd:(accession) gl:(accession) |
节点的类型
| attribute value | explanation |
| path:(accession) | pathway map ex) name=”path:map00040″ |
| ko:(accession) | KO (ortholog group) ex) name=”ko:E3.1.4.11″ |
| ec:(accession) | enzyme 酶 ex) name=”ec:1.1.3.5″ |
| rn:(accession) | reaction 反应 ex) name=”rn:R00120″ |
| cpd:(accession) | chemical compound 化合物 ex) name=”cpd:C01243″ |
| gl:(accession) | glycan 多糖 ex) name=”gl:G00166″ |
| [org prefix]:(accession) | gene product of a given organism 基因产物 ex) name=”eco:b1207″ |
| group:(accession) | complex of KOs 组 If accession is undefined, “undefined” is specified. ex) name=”group:ORC” |
节点关联的类型
attribute value | explanation | |
ECrel | enzyme-enzyme relation, indicating two enzymes catalyzing successive reaction steps | 酶与酶的关系,表明这两种酶催化逐次反应步骤 |
PPrel | protein-protein interaction, such as binding and modification | 蛋白质与蛋白质相互作用,比如绑定与修饰 |
GErel | gene expression interaction, indicating relation of transcription factor and target gene product | 基因表达的相互作用,表明转录因子与靶基因产物的关系 |
PCrel | protein-compound interaction | 蛋白质与化合物相互作用 |
maplink | link to another map | 链接到另一个图谱 |
关联或者相互作用的进一步明细
name | value | ECrel | PPrel | GErel | Explanation | |
compound | Entry element id attribute value for compound. | * | * | shared with two successive reactions (ECrel) or intermediate of two interacting proteins (PPrel) | 两个连续反应的共享复合物 另个相互作用蛋白质的中间体 | |
hidden compound | Entry element id attribute value for hidden compound. | * | shared with two successive reactions but not displayed in the pathway map | 隐含的复合物 | ||
activation | –> | * | positive and negative effects which may be associated with molecular information below | 激活 | ||
inhibition | –| | * | 抑制 | |||
expression | –> | * | interactions via DNA binding | 表达 | ||
repression | –| | * | 抑制 | |||
indirect effect | ..> | * | * | indirect effect without molecular details | 间接影响 | |
state change | … | * | state transition | 状态改变 | ||
binding/association | — | * | association and dissociation | 绑定或者结合 | ||
dissociation | -+- | * | 解离 | |||
missing interaction | -/- | * | * | missing interaction due to mutation, etc. | 由于突变,缺失的相互作用 | |
phosphorylation | +p | * | molecular events 分子水平 | 磷酸化 | ||
dephosphorylation | -p | * | 去磷酸化 | |||
glycosylation | +g | * | 糖基化 | |||
ubiquitination | +u | * | 泛素化 | |||
methylation | +m | * | 甲基化 |
数据的获取
所有的pathway信息,可以下载XML文件,解析XML文件可以得到该pathway的所有数据,如果只是需要部分数据,可以在程序中直接调用KEGG提供的API。



1F
请问,在kegg的代谢图中,eco为例的话,代谢中有特定物种的代谢图eco*****,还有map*****,那么在代谢图中连接到的map在eco中就不存在吗?还有就是白色和绿色的方框,特定物种的代谢图中,绿色就代表存在,白色就表示不存在么?
我在从KGML中提取酶关系,想建立一个酶的网络。求指教。 :razz:
2F
•Organism-specific pathway: green boxes are hyperlinked to GENES entries by converting K numbers (KO identifiers) to gene identifiers in the reference pathway, indicating the presence of genes in the genome and also the completeness of the pathway.
意思应该就是绿色表示存在,白色不存在吧。
不知道你说的map是像电路板一样的那个map,还是pathway里有框框的map,后者在选定了具体的pathway后就可以选择物种啊,通用的pathway的那张图应该是所有物种的合集吧。
KEGG页面的右上角一般都有Help,里面说的都挺详细的你可以看看。
B1
@ kiven 嗯,谢谢,还真没看过这个help以后要注意了。那在特定物种的代谢图里,绿色就存在,白色就不存在了。我说的那个map指的是,在eco00010这个代谢图里,有指向其他代谢途径的,比方说eco00020,这也是特定代谢图,还有的指向的途径是map打头的,比方说指向到了map00030,那么在Eco中就应该没有整个的这个map00030这个途径了吧 。 :razz:
3F
你可以看看这页说明
http://www.kegg.jp/kegg/document/help_pathway.html
有这么一句Each pathway is identified by a five-digit number preceded by one of: map, ko, ec, rn, and three- or four-letter organism code
介绍的是pathway map中节点的类型,其中有一种节点就是map,比如一个pathway_A中有一个分子M链接到了另外一个map(比如pathway_B),意思就是pathway_A中的分子M参与了pathway_B,当然你在pathway_B中也会看到分子M链接到了pathway_A
说的再简单点,比如丙酮酸在糖代谢中有,在氨基酸代谢中也有,当然就在两个图里都有啦,然后在糖代谢里丙酮酸就会有个链接到氨基酸代谢,反之一样。